乳糖消化不良
維基百科嘅醫學類文章只係提供參考,並唔係醫療意見。 閣下如果有任何關於健康嘅問題,請諮詢專業醫護人員。 |
| 乳糖消化不良 | |
|---|---|
| 同義詞 | 乳糖不耐 |
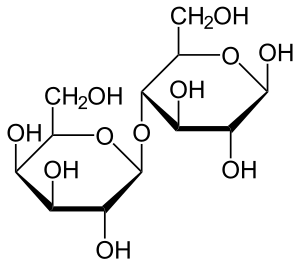 | |
| 乳糖嘅結構,佢係由兩個單糖構成 | |
| 病徵 | 肚痛, 肚脹, 肚屙, 心口悶 |
| 併發症 | 唔會損害消化道 |
| 通常發病 | 食完奶製品半個鐘到兩個鐘 |
| 起因 | 消化乳糖嘅能力降低咗 |
| 診斷 | 唔食含有乳糖嘅嘢啲症狀會消失 |
| 類似條件 | 乳糜瀉, 牛奶過敏 |
| 醫 | 減少食用含乳糖嘅食物,服用乳糖水解酵素 |
| 盛行率 | 全世界約莫六成五嘅人,東亞人超過九成 |
| 分類同拎 | |
| 醫學專科 | 胃腸科 |
| ICD-9-CM | 271.3 |
| OMIM | 223100 |
| DiseasesDB | 7238 |
| MedlinePlus | 000276 |
| eMedicine | 187249、930971 |
| Patient UK | 乳糖消化不良 |
| Orphanet | 319681 |
乳糖消化不良(粵拼:jyu5 tong4 siu1 faa3 bat1 loeng4),或稱乳糖不耐症(jyu5 tong4 bat1 noi6 zing3),係一種由於細路仔斷奶之後乳糖水解酶基因唔再表達而引起嘅一種消化不良[1][2]。乳糖不耐症並唔係一種病。之不過,基因突變可以令到乳糖水解酶基因喺細路仔斷奶之後重可以繼續表達出乳糖水解酶嚟到分解乳糖 [3]。亦即係講,大個咗消化唔到牛奶入邊嘅乳糖係一種正常嘅現象。正因為噉,乳糖不耐症英文又叫「Lactase non-persistence」。好多時,乳糖不耐症都會同先天性乳糖消化不良又或者細菌感染等外界因素引起嘅乳糖消化不良甚至牛奶過敏撈亂。
流行性
[編輯]乳糖不耐症唔會傳染,不過就喺大人當中好普遍,差唔多有六成半嘅大人喺斷奶後,乳糖水解酶基因嘅表達能力有唔同程度嘅降低。之不過,乳糖不耐症喺唔同嘅民族或者人種當中出現嘅百分比有好大差異。有超過九成比嘅東亞人有乳糖不耐症,而喺一尐歐洲國家,得一成左右嘅人有乳糖不耐症。詳細睇下邊個地圖同表:

| 民族或者人種 | 樣本數 | 乳糖不耐症嘅百分比 | 參攷 | 等位基因頻率 |
|---|---|---|---|---|
| 巴斯克人 | 85 | 0.3 | [4] | N/A |
| 荷蘭人 | N/A | 1 | [5] | N/A |
| 丹麥人 | N/A | 4 | [6] | N/A |
| 澳洲白人 | 160 | 4 | [7] | 0.20 |
| 瑞典人 | N/A | 5-7 | [8][9] | N/A |
| 英國人 | N/A | 5–15 | [10] | 0.184-0.302[11] |
| 日爾曼人 | 1805 | 6-23 | [12] | N/A |
| 瑞士人 | N/A | 10 | [7] | 0.316 |
| 美國白人 | 245 | 12 | [7] | 0.346 |
| 圖瓦雷克人 | N/A | 13 | [10] | N/A |
| 芬蘭人 | N/A | 14-23 | [13] | N/A |
| 東斯拉夫人(俄羅斯人、白俄羅斯人、烏克蘭人) | N/A | 15 | [14] | N/A |
| 奧地利人 | N/A | 15–20 | [10] | N/A |
| 西班牙人(非巴斯克) | N/A | 15 | [15] | N/A |
| 法國北部人 | N/A | 17 | [10] | N/A |
| 意大利中部人 | 65 | 19 | [16] | N/A |
| 印度人 | N/A | 20 | [17][18] | N/A |
| 非洲圖西人 | N/A | 20 | [7] | 0.447 |
| 非洲富拉尼人 | N/A | 23 | [7] | 0.48 |
| 貝都因人 | N/A | 25 | [10] | N/A |
| 成年葡萄牙人 | 102 | 35 | [19] | N/A |
| 意大利南部人 | 51 | 41 | [16] | N/A |
| 美國黑人細路 | N/A | 45 | [17] | N/A |
| 俄羅斯同埋芬蘭嘅薩米人 | N/A | 25–60 | [20] | N/A |
| 意大利北部人 | 89 | 52 | [16] | N/A |
| 西裔美國人 | N/A | 53 | [10] | N/A |
| 巴爾幹人 | N/A | 55 | [10] | N/A |
| 男性墨西哥裔美國人 | N/A | 55 | [17][18] | N/A |
| 克里特人 | N/A | 56 | [17] | N/A |
| 非洲馬賽人 | 21 | 62 | [21] | N/A |
| 法國南部人 | N/A | 65 | [10] | N/A |
| 希臘塞浦路斯人 | N/A | 66 | [17][18] | N/A |
| 米茲拉希猶太人 | N/A | 85 | [22] | N/A |
| 阿什肯納茲猶太人 | N/A | 68.8 | [17][18] | N/A |
| 塞法迪猶太人 | N/A | 62 | [22] | N/A |
| 也門猶太人 | N/A | 44 | [22] | N/A |
| 西西里島人 | 100 | 71 | [23][24] | N/A |
| 南美洲人 | N/A | 65–75 | [10] | N/A |
| 墨西哥農民 | N/A | 73.8 | [17][18] | N/A |
| 美國黑人 | 20 | 75 | [7] | 0.87 |
| 新疆北部哈薩克人 | 195 | 76.4 | [25] | |
| 黎巴嫩人 | 75 | 78 | [26] | N/A |
| 中亞人 | N/A | 80 | [10] | N/A |
| 阿拉斯加土著 | N/A | 80 | [17][18] | N/A |
| 澳洲土著毛利人 | 44 | 85 | [7] | 0.922 |
| 內蒙古人 | 198 | 87.9 | [25] | |
| 非洲班圖人 | 59 | 89 | [7] | 0.943 |
| 亞裔美國人 | N/A | 90 | [17][18] | N/A |
| 東北漢族人 | 248 | 92.3 | [25] | |
| 總體中國人 | 71 | 95 | [7] | 0.964 |
| 總體東南亞人 | N/A | 98 | [17][18] | N/A |
| 泰國人 | 134 | 98 | [7] | 0.99 |
| 美國印第安人 | 24 | 100 | [7] | 1.00 |
上邊數據嘅顯著性差異要睇樣本數。得乳糖不耐症嘅機會隨年齡嘅增加而增加。
症狀
[編輯]乳糖不耐症嘅好多症狀都係同腸有喇唥嘅,飲咗有乳糖嘅飲品之後好快就會發作,大約係半粒鐘到兩粒鐘咁上下。攝入咗嘅乳糖越多就會越唔舒服,而佢哋攝入少少乳糖一般都唔會出事,具體情況因人而異。例如日本人雖然好多都有乳糖不耐症,但係大部份人飲咗200ml都冇事。[27]幾乎冚嘭唥嘅病人都有肚痛同埋肚脹。其它嘅症狀就有放屁、嘔、反胃同埋肚痾,有時個肚仲會嘰哩咕嚕咁叫[1][28]。
起因
[編輯]乳糖不耐症係由乳糖水解酶基因嘅正常關閉所引起。至於呢個基因關閉嘅機理目前都未研究清楚[1]。乳糖水解酶基因一關閉,小腸就會無咗乳糖水解脢嘅分泌。因為乳糖水解酶係用來將乳糖分解成葡萄糖同埋半乳糖嘅一種酶,無咗佢就無辦法消化乳糖。乳糖一直去到大腸嗰度都未經過分解,噉大腸度尐細菌就會將部分乳糖發酵成乳酸,同時產生二氧化碳、甲烷同埋氫氣,所以有乳糖不耐症嘅人飲牛奶會放屁。而嗰尐未經分解嘅乳糖同埋其它未畀大小腸吸收嘅分子喺腸度積聚,濃度好高,因此尐水就會由毛細血管扯晒入條腸度,噉就會肚屙喇[29]。
發作時機
[編輯]乳糖不耐症嘅發作通常好早,一般細路哥斷奶之後就會有消化唔到牛奶嘅現象[1]。由兩到三歲開始,乳糖水解酶嘅表達數量就開始逐步降低,整個過程可能持續五到十年先至完成。因為噉,乳糖不耐症喺青少年同成年人入邊最普遍[2]。
診斷同醫法
[編輯]診斷
[編輯]好多有乳糖不耐症嘅人都會根據飲食同埋症狀嘅關係嚟自我診斷,但係準確嘅診斷重係要靠科學嘅方法,下邊列出咗幾重經常用到嘅診斷方法[30]:
- 氫呼吸測試
- 乳糖耐受性測試
- 乳糖耐受性測試係指畀個病人飲一定量嘅高乳糖嘅飲料,然後喺一定時間(通常唔使好耐)之後測病人嘅血糖,如果乳糖已經消化咗,就會分解成葡萄糖同半乳糖,而葡萄糖吸收咗之後就會喺血液度反映出嚟,噉病人嘅血糖就會高咗好多。有乳糖不耐症嘅人喺呢個測試入邊,佢哋嘅血糖唔會有明顯升高[30]。
- 腸組織檢視
- 腸組織檢視係指透過口腔內鏡喺十二指腸度攞些少組織出嚟,用一種叫「快速測試」嘅方法檢查組織入邊嘅乳糖水解酶活性。如果病人有乳糖不耐症,檢驗係查唔出有乳糖水解酶活性嘅[30]。
- 基因測試
- 基因測試係一種比氫呼吸測試慳皮嘅測試,而且佢嘅誤陰性比率比氫呼吸測試低尐。基因測試嘅做法係同病人抽血驗DNA,因為乳糖不耐症係同基因有關嘅,所以由DNA序列可以睇到有無乳糖不耐症嘅基因型[30]。
- 糞便酸度測試
喺診斷嘅時候,為咗攞到比較準確嘅結果,通常會用到唔止一種方法[30]。有乳糖消化不良嘅人做呢啲診斷嗰陣可能會引起好嚴重嘅肚痾,所以唔適合嬰幼兒使用。
醫法
[編輯]乳糖不耐症到而家為止都未有最徹底嘅醫法,不過只要一戒咗有乳糖成份嘅飲食,相關嘅症狀就自然會無咗。之不過,牛奶入邊嘅鈣質係唔少得嘅,有乳糖不耐症嘅人可以飲市面上嘅唔含乳糖嘅牛奶,又或者透過其它嘅飲食嚟補充鈣質[28]。至於直接食乳糖酵素嚟幫助消化嘅辦法而家已經好少用喇,因為市面上嘅唔含乳糖嘅牛奶已經解決咗呢個問題。上邊嘅內容只係用來參考,如果你懷疑自己有乳糖不耐症,最好搵醫生同營養師傾下。
雖然免咗含有乳糖嘅飲食能夠緩解所有由乳糖不耐症引起嘅症狀。之不過,飲少咗牛奶可能會引起缺鈣,因為牛奶係鈣質嘅主要來源[28]。鈣係維持生命唔少得嘅一樣嘢,因為鈣牽涉到神經傳遞素嘅釋放,肌肉嘅收縮,重有骨嘅結構。如果血入邊嘅鈣濃度低過正常水平,人體就會喺骨度扯鈣嚟維持正常水平。噉樣就會提高斷骨嘅風險[32]。
分子層面
[編輯]染色體
[編輯]乳糖水解酶基因係用來編碼乳糖水解酶蛋白嘅基因,佢嘅位置喺第二號人類染色體嘅長臂(q)入邊嘅第廿一號區域。呢個位置可以用「2q21」嚟表示[33][34]。亦可以睇下邊個圖:

第二號人類染色體係人類廿三對染色體入邊嘅一對。佢嘅大細係243,189,373(243Mb),入邊有3065個基因,編碼1,229種蛋白質[35][36]。
蛋白質
[編輯]乳糖水解酶
| |
| 識別 | |
| 符號 | LCT |
| 替換符號 | LAC; LPH; LPH1 |
| Entrez | 3938 |
| HUGO | 6530 |
| OMIM | 603202 |
| RefSeq | NM_002299 |
| UniProt | P09848 |
| 其他資料 | |
| EC編號 | 3.2.1.108 |
| 基因座 | 2 q21 |
同乳糖不耐症有關嘅蛋白質係乳糖水解酶,佢又叫做「乳糖酵素」。喺乳糖水解酶嘅催化作用底下,乳糖分解成葡萄糖同埋半乳糖,呢個化學反應可以用下邊個圖嚟表示:

突變
[編輯]- 乳糖水解酶基因嘅突變會搞到乳糖水解酶蛋白失效,噉就會引起新出世嬰孩嘅先天性乳糖消化不良[37]。之不過,呢度講嘅乳糖不耐症同先天性乳糖消化不良係兩碼事嚟[38]。前邊講咗,基因突變可以令到乳糖水解酶基因係細路仔斷奶之後重可以繼續表達出乳糖水解酶嚟到分解乳糖。呢個突變嘅基因唔係乳糖水解酶基因本身,而係乳糖水解酶基因上游隔離嘅一個叫「MCM6」嘅基因嘅一個內含子發生嘅突變[39]。呢種變異喺歐洲出現。MCM6基因嘅C/T 13910突變係斷奶之後重可以繼續表達出乳糖水解酶嘅主要原因。喺呢度,「C/T」即係由胸腺嘧啶(T)變成胞嘧啶(C),而「13910」表示呢個突變嘅位置喺乳糖水解酶基因上游13.9kb嘅位置。之不過,乳糖水解酶基因係點樣關閉嘅,就重未研究清楚[38]。
參攷
[編輯]- ↑ 1.0 1.1 1.2 1.3 Matthews SB, Waud JP, Roberts AG; 等 (2005). "Systemic lactose intolerance: a new perspective on an old problem" (PDF). Postgrad Med J. 81: 167–173.
{{cite journal}}: Explicit use of et al. in:|author=(help)CS1 maint: multiple names: 作者名單 (link) - ↑ 2.0 2.1 R. Bowen. (2009). "Lactose Intolerance (Lactase Non-Persistence)". Hypertexts for Biomedical Sciences. 原著喺2010年6月23號歸檔. 喺2011年6月19號搵到.
- ↑ Bulhões AC, Goldani HA, Oliveira FS, Matte US, Mazzuca RB, Silveira TR. (2007). "Correlation between lactose absorption and the C/T-13910 and G/A-22018 mutations of the lactase-phlorizin hydrolase (LCT) gene in adult-type hypolactasia". Braz J Med Biol Res.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ Enattah, N; Trudeau, A; Pimenoff, V; Maiuri, L; Auricchio, S; Greco, L; Rossi, M; Lentze, M; Seo, J (2007). "Evidence of Still-Ongoing Convergence Evolution of the Lactase Persistence T-13910 Alleles in Humans". The American Journal of Human Genetics. 81: 615–25. doi:10.1086/520705. PMID 17701907.
- ↑ Flatz G (1987). "Genetics of lactose digestion in humans". Adv. Hum. Genet. 16: 1–77. PMID 3105269.
- ↑ Timo Sahi (N/A). "Genetics and epidemiology of adult-type hypolactasia with emphasis on the situation in Europe". Scandinavian Journal of Nutrition/Naringsforskning.
{{cite news}}: Check date values in:|date=(help) - ↑ 7.00 7.01 7.02 7.03 7.04 7.05 7.06 7.07 7.08 7.09 7.10 Kretchmer N (1972). "Lactose and lactase". Sci. Am. 227 (4): 71–8. PMID 4672311.
- ↑ Almon, R; Engfeldt, P; Tysk, C; Sjöström, M; Nilsson, TK (2007). "Prevalence and trends in adult-type hypolactasia in different age cohorts in Central Sweden diagnosed by genotyping for the adult-type hypolactasia-linked LCT -13910C > T mutation". Scandinavian journal of gastroenterology. 42 (2): 165–70. doi:10.1080/00365520600825257. PMID 17327935.
- ↑ Torniainen, S.; Hedelin, M.; Autio, V.; Rasinpera, H.; Balter, K. A.; Klint, A.; Bellocco, R.; Wiklund, F.; Stattin, P. (2007). "Lactase Persistence, Dietary Intake of Milk, and the Risk for Prostate Cancer in Sweden and Finland". Cancer Epidemiology Biomarkers & Prevention. 16: 956. doi:10.1158/1055-9965.EPI-06-0985. PMID 17507622.
- ↑ 10.00 10.01 10.02 10.03 10.04 10.05 10.06 10.07 10.08 10.09 de Vrese M, Stegelmann A, Richter B, Fenselau S, Laue C, Schrezenmeir J (2001). "Probiotics--compensation for lactase insufficiency". Am. J. Clin. Nutr. 73 (2 Suppl): 421S–429S. PMID 11157352.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ G.D. Smith et al., Lactase persistence-related genetic variant: population substructure and health outcomes. European Journal of Human Genetics, 2008.
- ↑ Flatz, G.; Howell, J.N.; Doench, J.; Flatz, S.D. (1982). "Distribution of physiological adult lactase phenotypes, lactose absorber and malabsorber, in Germany". Human Genetics. 62 (2): 152–7. doi:10.1007/BF00282305. PMID 6819221.
- ↑ Heli Rasinperä (April 2006). "ADULT-TYPE HYPOLACTASIA: Genotype-phenotype correlation" (PDF). 原著 (PDF)喺2012年4月1號歸檔. 喺2011年6月19號搵到.
- ↑ Valenkevich LN, Iakhontova OI (2005). "[Prevalence of the lactase deficiency among the population of the northwestern region of Russia]". Eksp Klin Gastroenterol (Russian) (1): 97–100, 108. PMID 15991859.
{{cite journal}}: CS1 maint: unrecognized language (link) - ↑ http://yannklimentidis.blogspot.com/2007/03/monday-maps-lactase-persistence-in.html
- ↑ 16.0 16.1 16.2 Cavalli-Sforza LT, Strata A, Barone A, Cucurachi L (1987). "Primary adult lactose malabsorption in Italy: regional differences in prevalence and relationship to lactose intolerance and milk consumption" (PDF). Am. J. Clin. Nutr. 45 (4): 748–54. PMID 3565303.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ 17.00 17.01 17.02 17.03 17.04 17.05 17.06 17.07 17.08 17.09 Enattah NS, Sahi T, Savilahti E, Terwilliger JD, Peltonen L, Järvelä I (2002). "Identification of a variant associated with adult-type hypolactasia". Nat. Genet. 30 (2): 233–7. doi:10.1038/ng826. PMID 11788828.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ 18.0 18.1 18.2 18.3 18.4 18.5 18.6 18.7 "Lactose Intolerance: The Molecular Explanation". UC Davis Nutritional Genomics.
- ↑ (葡萄牙文) Intolerância à lactose 互聯網檔案館嘅歸檔,歸檔日期2010年8月15號,. Maria do Céu Salgado - Outubro de 2007
- ↑ Kozlov A, Lisitsyn D (1997). "Hypolactasia in Saami subpopulations of Russia and Finland". Anthropol Anz. 55 (3–4): 281–7. PMID 9468755.
- ↑ Jackson RT, Latham MC (1979). "Lactose malabsorption among Masai children of East Africa". Am. J. Clin. Nutr. 32 (4): 779–82. PMID 581925.
- ↑ 22.0 22.1 22.2 Ernest L. Abel (August 2001). Jewish Genetic Diseases: a Layman's Guide. McFarland & Company, Inc., Publishers. ISBN 9780786409419.
- ↑ Burgio GR, Flatz G, Barbera C; 等 (1984). "Prevalence of primary adult lactose malabsorption and awareness of milk intolerance in Italy" (PDF). Am. J. Clin. Nutr. 39 (1): 100–4. PMID 6691285.
{{cite journal}}: Explicit use of et al. in:|author=(help)CS1 maint: multiple names: 作者名單 (link) - ↑ Vesa TH, Marteau P, Korpela R (2000). "Lactose intolerance". J Am Coll Nutr. 19 (2 Suppl): 165S–175S. PMID 10759141. 原著喺2010年5月28號歸檔. 喺2011年6月19號搵到.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ 25.0 25.1 25.2 Wang YG, Yan YS, Xu JJ; 等 (1984). "Prevalence of primary adult lactose malabsorption in three populations of northern China". Hum. Genet. 67 (1): 103–6. doi:10.1007/BF00270566. PMID 6235167.
{{cite journal}}: Explicit use of et al. in:|author=(help)CS1 maint: multiple names: 作者名單 (link) - ↑ Nasrallah SM (1979). "Lactose intolerance in the Lebanese population and in "Mediterranean lymphoma"" (PDF). Am. J. Clin. Nutr. 32 (10): 1994–6. PMID 484518.
- ↑ Yoshida, Y.; Sasaki, G.; Goto, S.; Yanagiya, S.; Takashina, K. (1975). "Studies on the etiology of milk intolerance in Japanese adults". Gastroenterologia Japonica. 10 (1): 29–34. doi:10.1007/BF02775921. ISSN 0435-1339. PMID 1234085.
- ↑ 28.0 28.1 28.2 "Lactose Intolerance". National Digestive Diseases Information Clearinghouse. 2009. 原著喺2011年6月22號歸檔. 喺2011年6月19號搵到.
- ↑ Grant, M. (2005). "Lactose intolerance". Biological Sciences Review. 17: 28–31.
{{cite journal}}: Cite has empty unknown parameter:|1=(help) - ↑ 30.0 30.1 30.2 30.3 30.4 30.5 Kathleen Marchiondo. (2009). "Lactose Intolerance: a Nursing Perspective". MedSurg Nursing. 18: 9–16.
- ↑ "Stool Acidity Test". Jay W. Marks, M.D. 喺2011-05-20搵到.
- ↑ Jane B. Reece (2011). Cambell Biology, Ninth Edition.
{{cite book}}: Cite has empty unknown parameter:|1=(help) - ↑ "Genetics Home Reference". 2011. 原著喺2010年3月8號歸檔. 喺2011年6月20號搵到.
{{cite journal}}: Cite journal requires|journal=(help) - ↑ 34.0 34.1 "National Center for Biotechnology Information. Master Map Ideogram". 2011.
{{cite journal}}: Cite journal requires|journal=(help); Cite has empty unknown parameter:|1=(help) - ↑ "International Human Genome Consortium. Initial sequencing and analysis of the human genome". Nature. 409: 860–921. 2011.
{{cite journal}}: Cite has empty unknown parameter:|1=(help) - ↑ "The Vertebrate Genome Annotation (VEGA) database". '. 2011.
- ↑ Suvi Torniainen, Roberta Freddara, Taina Routi, Carolien Gijsbers, Carlo Catassi, Pia Höglund, Erkki Savilahti and Irma Järvelä. (2009). "Four novel mutations in the lactase gene (LCT) underlying congenital lactase deficiency (CLD)". BMC Gastroenterology.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ 38.0 38.1 Bulhões AC, Goldani HA, Oliveira FS, Matte US, Mazzuca RB, Silveira TR. (2007). "Correlation between lactose absorption and the C/T-13910 and G/A-22018 mutations of the lactase-phlorizin hydrolase (LCT) gene in adult-type hypolactasia". Braz J Med Biol Res. 40: 1441–1446.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ Krisztián Bácsi, Erika Hitre, János P Kósa, Henrik Horváth, Áron Lazáry, Péter L Lakatos, Bernadett Balla, Barna Budai, Péter Lakatos and Gábor Speer. (2008). "Effects of the lactase 13910 C/T and calcium-sensor receptor A986S G/T gene polymorphisms on the incidence and recurrence of colorectal cancer in Hungarian population". BMC Cancer.
{{cite journal}}: CS1 maint: multiple names: 作者名單 (link) - ↑ NICHOLAS WADE. (2006). "Lactose Tolerance in East Africa Points to Recent Evolution". The New York Times.
